Pracownia Przetwarzania i Analizy Obrazów Mikroskopowych
Zespół

dr hab. Anna Korzyńska, profesor IBIB PAN – kierownik Pracowni
dr inż. Łukasz Roszkowiak,
mgr inż. Antonina Pater
mgr inż. Shrief Abdelazeez
lek. med. Krzysztof Siemion
mgr inż. Jakub Żak
Jesteśmy małym, interdyscyplinarnym zespołem opracowującym innowacyjne metody analizy obrazów mikroskopowych próbek biologicznych, przyczyniając się do rozwoju diagnostyki, prognozowania i badań biomedycznych.
Obszary zainteresowań:
- Zaawansowane przetwarzanie obrazu – opracowujemy metody analizy wybarwionych skrawków tkanek i rozmazów komórkowych, poprawiając precyzję diagnostyczną i udoskonalając modele predykcyjne.
- Udoskonalanie technik analizy obrazu przy użyciu metod tradycyjnych i uczenia maszynowego.
- Łączenie biologii i uczenia maszynowego – integrując klasyczne techniki analizy obrazu z uczeniem maszynowym, ulepszamy interpretację obrazów w medycynie i naukach przyrodniczych.
Łącząc wiedzę z zakresu biologii, informatyki i analizy danych, stosujemy multidyscyplinarne podejście do rozwiązywania złożonych wyzwań badawczych.
Opracowujemy również zestawy danych z adnotacjami ekspertów, niezbędne do rozwoju uczenia maszynowego w zastosowaniach biomedycznych. Niektóre z nich, jak zbiór danych Bialystok (fragmenty rozmazów badań przesiewowych w kierunku raka szyjki macicy), są publicznie dostępne pod adresem https://ibib.waw.pl/nauka/zaklady-pracownie/zaklad-i-pracownia-2/boacd/ i opisane w publikacji:
- Antonina Pater, Krzysztof Siemion, Karol Deptuch, Łukasz Roszkowiak, Jakub Żak, Katarzyna Jakubowska, Stanisław Sulkowski, Marek Baltaziak, Mariusz Koda, Anna Korzyńska (2023) „Conventional Cervical Cytology Image Dataset with Cell Outline Annotations”, 2023 International Symposium on Image and Signal Processing and Analysis (ISPA), Rome, Italy, 2023, pp. 1-6, DOI: 10.1109/ISPA58351.2023.10279274
Zbiór danych Białystok składa się ze 162 obrazów (3500×3500 px) zawierających 2419 adnotowanych komórek szyjki macicy, sklasyfikowanych zgodnie ze skalą Bethesda. Obrazy zostały wyodrębnione z obrazów całych wirtualnych slajdów (WSI) rutynowych rozmazów szyjki macicy, zapewniając różnorodną i realistyczną reprezentację rzeczywistych próbek.
Zestaw danych obejmuje pełne spektrum zmienności cytologicznej, od wyraźnie rozróżnialnych komórek po trudne przypadki – w tym zabarwiony śluz, gęsto upakowane ciemne skupiska komórek i obfite neutrofile, które przesłaniają widoczność. Zbiór danych zawiera etykiety cytoplazmy podzielone na sześć klas Bethesda i dwie dodatkowe grupy: niezidentyfikowane komórki i niezidentyfikowane skupiska komórek. Te dodatkowe kategorie wynikają z nieodłącznej niepewności w cytodiagnostyce, gdzie niektóre komórki nie mogą być ostatecznie sklasyfikowane, ale pozostają możliwe do segmentacji i analizy.
Kluczowe cechy:
- realistyczne fragmenty wymazu z szyjki macicy, odzwierciedlające rutynową praktykę cytologiczną;
- etykiety zgodne z systemem Bethesda, zapewniające przydatność kliniczną;
- wszechstronność w zadaniach segmentacji, klasyfikacji i wykrywania;
- stanowi wymagający test porównawczy, zaprojektowany w celu wspierania rozwoju nowoczesnych modeli AI.
W temacie zaawansowanego przetwarzania obrazu ukazały się następujące publikacje:
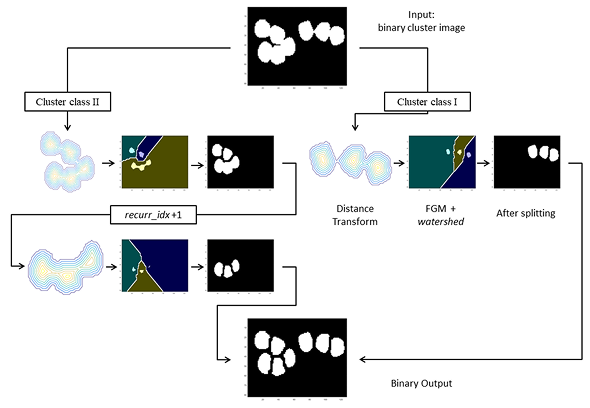
- Lukasz Roszkowiak, Anna Korzynska, Krzysztof Siemion, Jakub Zak, Dorota Pijanowska, Ramon Bosch, Marylene Lejeune & Carlos Lopez (2021) “System for quantitative evaluation of DAB&H-stained breast cancer biopsy digital images (CHISEL)”, Sci Rep 11, 9291 (2021). DOI: 10.1038/s41598-021-88611-y [IF 4.380, 140 pkt. MNiSW]
CHISEL (Computer-assisted Histopathological Image Segmentation and EvaLuation) to kompleksowy system przeznaczony do ilościowej analizy zdigitalizowanych próbek biopsji raka piersi barwionych metodą DAB&H. Charakteryzuje się wykorzystaniem strategii minimalizowania utraty obiektów na krawędzi obszaru zainteresowania, dzieleniem klastrów jąder i korygowaniem niedokładnych konturów, wykorzystując uczenie maszynowe i rekurencyjne lokalne przetwarzanie transformaty odległościowej. Został zweryfikowany na oznaczonych zestawach danych raka piersi i wykazał wydajność porównywalną z istniejącymi najnowocześniejszymi metodami. Jego przyjazny dla użytkownika interfejs jest zoptymalizowany pod kątem wydajnych obliczeń, dzięki czemu jest dostępny dla użytkowników o ograniczonych zasobach w porównaniu do tych wymaganych przez typowe techniki głębokiego uczenia.

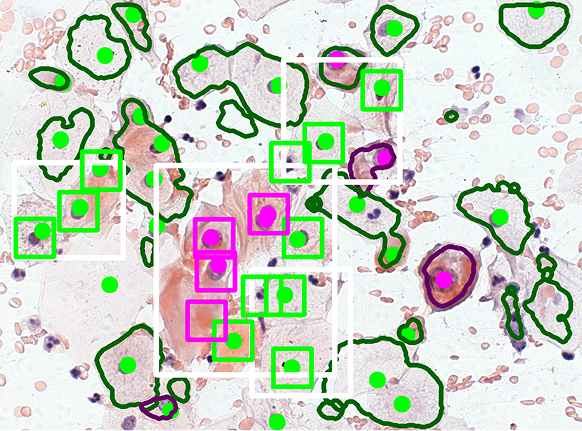
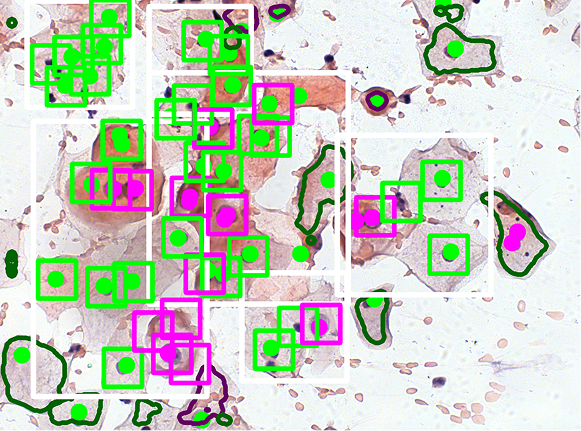
- Antonina Pater, Łukasz Roszkowiak, Jakub Żak, Krzysztof Siemion, Anna Korzyńska, “An application of U-Net for cell detection in fragments of cytological smear images”, Proceedings of the 3rd Polish Conference on Artificial Intelligence, 2022, str. 185-189, IBSN 978-83-7421-401-8
Cytologia szyjki macicy jest zwykle oceniana ręcznie poprzez identyfikację komórek ze zmianami przedrakowymi. Bethesda System for Reporting Cervical Cytology, uznany na całym świecie system raportowania, kategoryzuje płaskonabłonkowe zmiany śródnabłonkowe na dwa typy: płaskonabłonkowe zmiany śródnabłonkowe niskiego stopnia (LSIL) i płaskonabłonkowe zmiany śródnabłonkowe wysokiego stopnia (HSIL). Komórki bez nieprawidłowości są klasyfikowane jako negatywne dla zmian śródnabłonkowych (NILM).
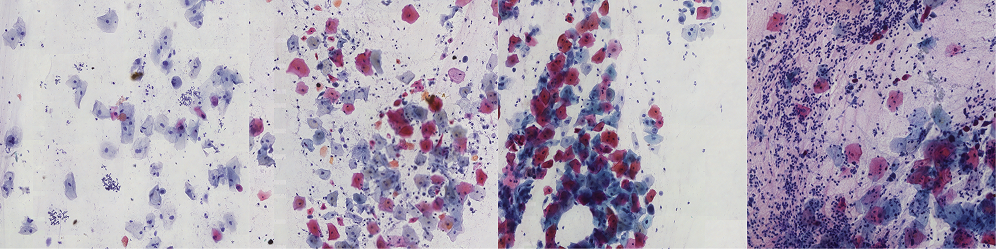
Opracowaliśmy metodę klasyfikacji wstępnie wysegmentowanych komórek i jąder przy użyciu modelu opartego na VGG16. Aby poprawić możliwości szkolenia, zastosowaliśmy technikę augmentacji opartą na metodzie GAN opracowaną w naszym laboratorium. Poniższe obrazy ilustrują wyniki klasyfikacji uzyskane po segmentacji i procesie deklasteryzacji.


- Antonina Pater, Łukasz Roszkowiak, Krzysztof Siemion, Anna Korzyńska (2021) „Estimation of the fraction of area covered by cells and cell clusters in WSI patches”. XXII Krajowa Konferencja Biocybernetyki i Inżynierii Biomedycznej, Warszawa, 19-21.05.2021.
- Jakub Żak, Krzysztof Siemion, Lukasz Roszkowiak, Anna Korzynska L (2021) „Fourier Transform Layer for Fast Forground Segmantation in Samples’ Images of Tissue Biopsies”) XXII Krajowa Konferencja Biocybernetyki i Inżynierii Biomedycznej, Warszawa, 19-21.05.2021.
- Krzysztof Siemion, Anna Korzyńska, Łukasz Roszkowiak, Jakub Żak, Antonina Pater, Joanna Reszeć-Giełażyn (2021) „Application of image analysis methods to evaluate histopathological slides in the study of prognostic factors of inflammatory spindle cell lesions” XXII Krajowa Konferencja Biocybernetyki i Inżynierii Biomedycznej, Warszawa, 19-21.05.2021
- Łukasz Roszkowiak, Jakub Zak, Krzysztof Siemion, Antonina Pater, Anna Korzynska (2021) „Split point assessment for HRnet dual model” XXII Krajowa Konferencja Biocybernetyki i Inżynierii Biomedycznej, Warszawa, 19-21.05.2021
W temacie udoskonalania technik analizy obrazu ukazały się następujące publikacje:
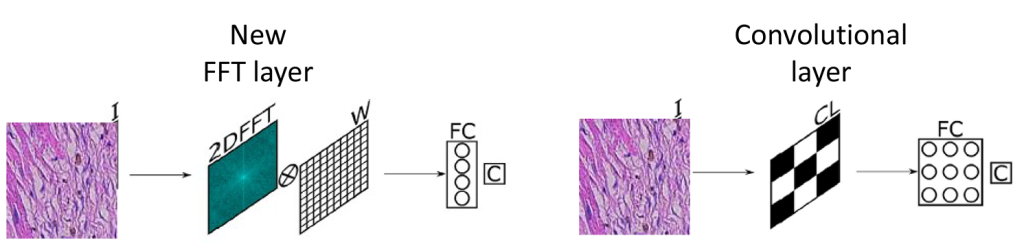
- Jakub Zak, Anna Korzynska, Antonina Pater, Lukasz Roszkowiak (2023) „Fourier Transform Layer: A proof of work in different training scenarios” Applied Soft Computing, 145, 110607. DOI: 10.1016/j.asoc.2023.110607 [IF 8,7; 200 pkt. MNiSW]

W artykule przedstawiono nowatorskie podejścia, które wykorzystuje połączoną sieć neuronową (NN) przetwarzającą transformatę Fouriera obrazów zamiast samych obrazów. Modele składające się wyłącznie z opracowanej warstwy szybkiej transformaty Fouriera (FFT) zostały wytrenowane do klasyfikowania obrazów z publicznie dostępnych zbiorów danych. Wyniki klasyfikacji zostały następnie porównane z wynikami prostszych modeli, które zawierały tylko jedną warstwę konwolucyjną. Do porównania wykorzystano takie wskaźniki, jak dokładność testu, obszar pod krzywą (AUC) i czas szkolenia. Wyniki wskazały, że modele wykorzystujące proponowaną warstwę FFT osiągnęły dokładność testową porównywalną z modelami konwolucyjnymi – 96% w porównaniu do 98% – wykazując jednocześnie co najmniej 27% redukcję czasu szkolenia na epokę, gdy są uruchamiane na procesorze (CPU), bez wykorzystania procesora karty graficznej (GPU).
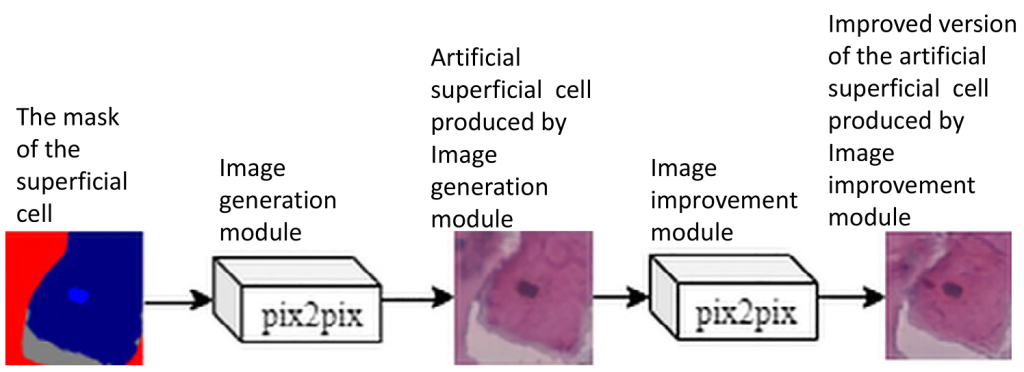
- Jakub Zak, Michal K. Grzeszczyk, Antonina Pater, Lukasz Roszkowiak, Krzysztof Siemion, Anna Korzynska (2022) „Cell image augmentation for classification task using GANs on Pap smear dataset”, Biocybernetics and Biomedical Engineering 42(3), pp 995–1011; DOI:10.1016/j.bbe.2022.07.003 [IF 5,667; 140 pkt. MNiSW]

Generative Adversarial Networks (GAN) tworzą sztuczne obrazy, które są trudne do odróżnienia od rzeczywistych używanych podczas treningu. Włączenie tych sztucznych obrazów do procesu uczenia konwolucyjnych sieci neuronowych (CNN) w celu wykrywania, segmentacji lub klasyfikacji obiektów na obrazach usprawnia szkolenie modelu i ostatecznie poprawia wydajność wnioskowania. Jest to szczególnie istotne w przypadku analizy obrazów medycznych, która podlega ścisłym regulacjom prawnym i etycznym. W artykule zaproponowano dwuetapową metodę sztucznej syntezy obrazu opartą na architekturze sieci pix2pix. Zaproponowana metoda, zweryfikowana na zbiorze danych klasyfikacji komórek wymazu z szyjki macicy, wykazała wzrost wydajności, szczególnie w zakresie dokładności klasyfikacji.
- Anna Korzynska, Lukasz Roszkowiak, Jakub Zak, Krzysztof Siemion (2021) “A review of current systems for annotation of cell and tissue images in digital pathology” Biocybernetics and Biomedical Engineering vol 41, pp 1436-1453 [IF 4.314; 140 pkt. MNiSW]

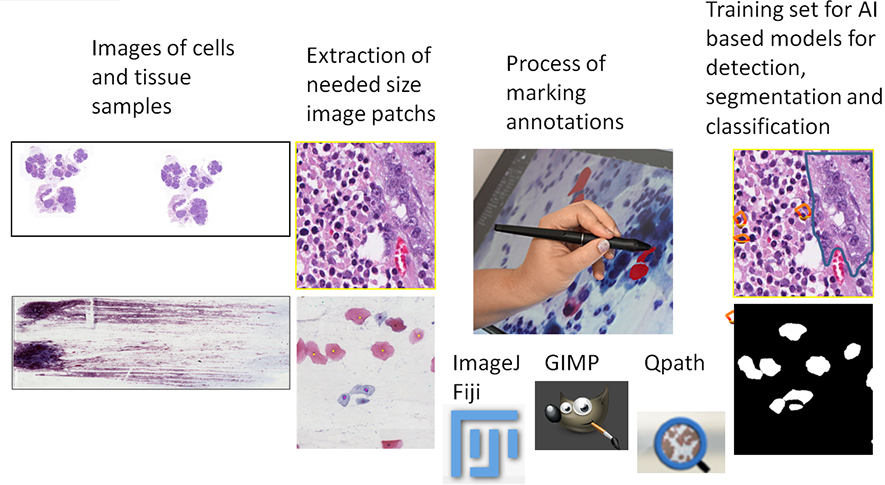
Znaczącym ograniczeniem w komputerowo wspomaganych systemach diagnostycznych dla patologii jest wysoki koszt etykietowania danych. Ocena próbek tkankowych (histopatologicznych) i komórkowych (cytologicznych) stanowi złożone wyzwanie. Aby usprawnić pracochłonny proces gromadzenia wystarczająco dużego zbioru danych, różne systemy: GIMP, QuPath, ImageJ mogą być wykorzystane do adnotacji obrazu.
- Krzysztof Siemion, Lukasz Roszkowiak, Jakub Zak, Antonina Pater, Anna Korzynska (2024) Tissue Pattern Classification with CNN in Histological Images. In: Strumiłło, P., Klepaczko, A., Strzelecki, M., Bociąga, D. (eds) The Latest Developments and Challenges in Biomedical Engineering. PCBEE 2023. Lecture Notes in Networks and Systems, vol 746. Springer, Cham. DOI: 10.1007/978-3-031-38430-1_2
- Shrief Abdelazeez, Lukasz Roszkowiak, Krzysztof Siemion, Carlos Lopez, Marylene Lejeune, Anna Korzynska (2023) „T regulatory Lymphocyte Nuclei Segmentation in DAB – Stained Breast Cancer Biopsy Digital Images Using Deep Learning Algorithms”; in Book of Abstracts – Polish Conference on Biocybernetics and Biomedical Engineering (PCBEE) Ed. Paweł Strumiłło, Artur Klepaczko, Michał Strzelecki, Bociąga, pp 41
- Jakub Zak, Krzysztof Siemion, Lukasz Roszkowiak, Anna Korzynska (2022) „Fourier Transform Layer for Fast Forground Segmantation in Samples’ Images of Tissue Biopsies”, in Biocybernetics and Biomedical Engineering – Current Trends and Challenges Ed. D. Pijanowska, K. Zieliński, A. Liebert, J Kacprzyk; Lecture Notes in Networks and Systems 293, pp 118-125, Springer 2022 DOI: 10.1007/978-3-030-83704-4
W temacie łączenia biologii i uczenia maszynowego ukazały się następujące publikacje:
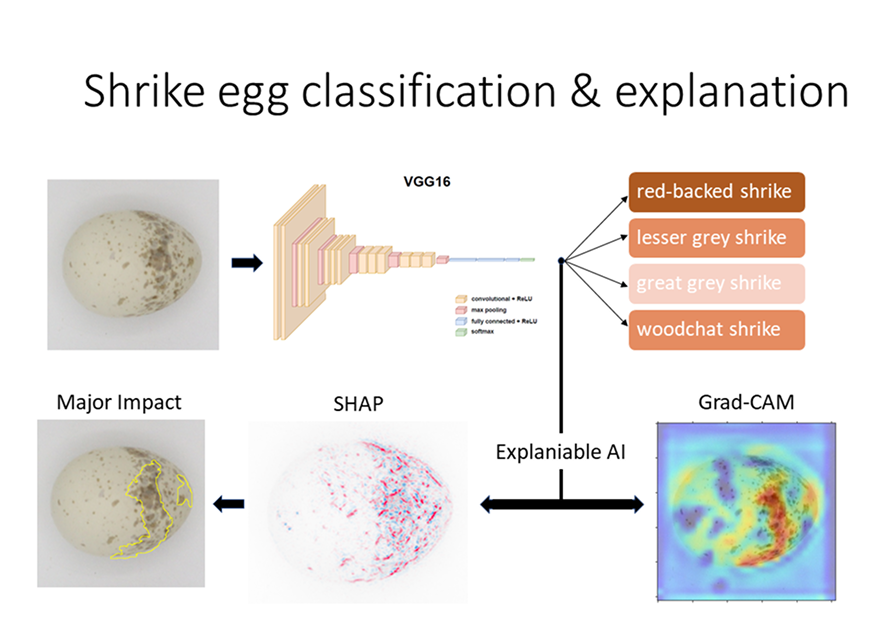
- Paweł Pstrokoński, Lukasz Roszkowiak, Anna Korzyńska, Wojeciech Wójcik, Martin Packert, Joanna Rosenberger, Dominika Mierzwa-Szymkowiak, Magdalena Seplowska, Jan Lontkowski, Marek Słupek, Krzysztof Damaziak (2025) “Can Explainable AI classify shrike (Laniidae) eggs by uncovering species-wide pigmentation patterns?” PLOS ONE accepted, [IF 2.9; 100 pkt. MNiSW]

Can Explainable AI classify shrike (Laniidae) eggs by uncovering species-wide pigmentation patterns?
Komputerowa analiza pigmentacji jaj może ujawnić wzorce identyfikacyjne dla gatunków ptaków, co przyczyni się do weryfikacji hipotez badawczych. Badania prowadzone są na sfotografowanych okazach archiwalnych jaj (wydmuszek) należących do jednego rodzaju Lanius z jego 5 gatunkami. Przeprowadzono systematyczną analizę skuteczności klasyfikacji przy użyciu głębokiej sieci konwolucyjnej VGG16. Porównano wpływ różnych strategii augmentacji obrazu i wykorzystując zdobytą wiedzę zrównoważono zbiór danych uzyskując ostatecznie dokładność powyżej 95% na zbiorze testowym.
W badaniu tym zastosowano interpretowalną sztuczną inteligencję (ang. Explainable Artificial Intelligence) do analizy wzorców pigmentacji jaj ptaków. Aby odkryć sygnatury identyfikacyjne dla całego gatunku, zastosowano metody Grad-CAM i SHAP, ukazujące regiony obrazu najbardziej wpływające na klasyfikację. Choć nie udało się zidentyfikować konkretnych cech dyskryminacyjnych, wskazały one ogólne trendy. Opracowane narzędzie poprawia organizację kolekcji muzealnych, weryfikację gatunków i dokładność badań oologicznych, oferując jednocześnie wgląd w ewolucję ptaków, strategie ekologiczne i potencjalne zastosowania biomedyczne.

EGGS to specjalistyczne podejście do przetwarzania obrazu zaprojektowane w celu stworzenia znormalizowanego i wysokiej jakości zbioru danych obrazów jaj ptaków. Integruje zaawansowane przetwarzanie wstępne, wykrywanie orientacji i usuwanie uszkodzonych okazów w celu poprawy analizy danych oologicznych. Łącząc te techniki z modelami głębokiego uczenia, EGGS usprawnia badania oologiczne, oferując precyzyjne etykietowanie obrazów jaj. Zbiór danych utworzony za pomocą EGGS służy jako cenne źródło do badań ornitologicznych, umożliwiając głębszy wgląd w reprodukcję ptaków, ewolucję i adaptację środowiskową.
- Łukasz Roszkowiak, Paweł Pstrokoński, Wojeciech Wójcik, Krzysztof Damaziak, Anna Korzyńska (2025) „EGGS: Efficient Gathering and Structuring of Avian Egg Datasets”, 24th Polish Conference on Biocybernetics and Biomedical Engineering conference, Warsaw, 16-18.06.2025
Ponadto ukazały się następujące artykuły:
We współpracy z Uniwersytetem Medycznym w Białymstoku:
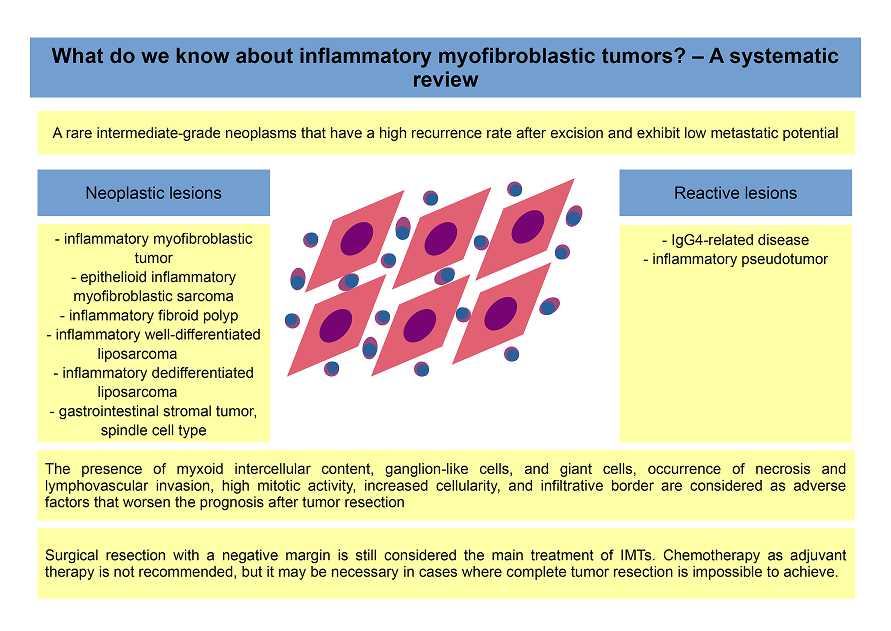
- Krzysztof Siemion, Joanna Reszec-Gielazyn, Joanna Kisluk, Lukasz Roszkowiak, Jakub Zak, Anna Korzynska: „What do we know about inflammatory myofibroblastic tumors? – A systematic review” Advances in Medical Sciences 67 (1), 2022 pp.129–138 DOI: 0.1016/j.advms.2022.02.002, [IF 2,852, 100pkt ]

Opracowany przegląd, systematycznie bada aktualny stan wiedzy na temat zapalnych guzów miofibroblastycznych (IMT), rzadkich nowotworów mezenchymalnych o zmiennym zachowaniu klinicznym. Podsumowuje kluczowe odkrycia związane z ich patogenezą, cechami histopatologicznymi, wyzwaniami diagnostycznymi i strategiami leczenia. W przeglądzie podkreślono również ostatnie postępy w genetyce molekularnej, w szczególności rearanżacje genu ALK, które mają ważne implikacje diagnostyczne i terapeutyczne.
We współpracy z Research in Oncological Pathology and Bioinformatics (PO&B) (wcześniej Molecular Biology and Research Section), Institut d’Investigacio Sanitaria Pere Virgili (IISPV), URV, Hiszpania:
- Marylène Lejeune, Benoît Plancoulaine, Nicolas Elie, Ramon Bosch, Laia Fontoura, Izar de Villasante, Anna Korzyńska; at all (2021) “How the variability between computer-assisted analysis procedures evaluating immune markers can influence patients’ outcome prediction”; Histochemistry and Cell Biology; DOI: 10.1007/s00418-021-02022-8 [IF 4.304, 100pkt ]
- Carlos López, Albert Gibert-Ramos, Ramón Bosch, Anna Korzynska, Marcial García-Rojo, Gloria Bueno, Joan Francesc García-Fontgivell, Salomé Martínez González, Laia Fontoura, Andrea Gras Navarro, Esther Sauras Colón, Júlia Casanova Ribes, Lukasz Roszkowiak, Albert Roso, Marta Berenguer, Montserrat Llobera, Jordi Baucells, Marylène Lejeune (2021) “Differences in the Immune Response of the Nonmetastatic Axillary Lymph Nodes between Triple-Negative and Luminal A Breast Cancer Surrogate Subtypes” American Journal of Pathology (2021) Volume 191, Issue 3, March 2021, Pages 545-554 DOI: 10.1016/j.ajpath.2020.11.008 [IF 4.307, 140pkt MNiSW]
- Carlos López, Ramón Bosch, Anna Korzynska,·Marcial García-Rojo, Gloria Bueno, Joan Francesc García Fontgivell, Salomé Martínez González, Andrea Gras Navarro, Esther Sauras Colón, Júlia Casanova Ribes, Lukasz Roszkowiak, Daniel Mata, Meritxell Arenas, Junior Gómez, Albert Roso, Marta Berenguer, Silvia Reverté Villarroya, Montserrat Llobera, Jordi Baucells, Marylène Lejeune () „CD68 and CD83 immune populations in non metastatic axillary lymph nodes are of prognostic value for the survival and relapse of breast cancer patients”, Breast Cancer 29(4) pp.618-635 DOI: 10.1007/s12282-022-01336-2, [IF 3.303; 70pkt MNiSW]
- Marylène Lejeune, Laia Reverté, Esther Sauras, Noèlia Gallardo, Ramon Bosch, Albert Roso, Anna Petit, Vicente Peg, Francisco Riu, Joan García-Fontgivell, José Ibáñez, Fernanda Relea,Begoña Vieites, Catherine Bor, Luis de la Cruz-Merino, Meritxell Arenas, Valerie Rodriguez, Juana Galera, Anna Korzynska, Philippe Belhomme, Benoît Plancoulaine, Tomás Álvaro and Carlos López (2023) „Prognostic Implications of the Residual Tumor Microenvironment after Neoadjuvant Chemotherapy in Triple-Negative Breast Cancer Patients without Pathological Complete Response”, Cancers 2023, 15, 597. DOI: 10.3390/cancers15030597 [IF 5,2; 200 pkt. MNiSW]
- Marylène Lejeune, Laia Reverté, Noèlia Gallardo, Esther Sauras, Ramon Bosch 1 , Daniel Mata, Albert Roso, Anna Petit, Vicente Peg, Francisco Riu, Joan García-Fontgivell, Fernanda Relea, Begoña Vieites, Luis de la Cruz-Merino, Meritxell Arenas, Valeri Rodriguez, Juana Galera, Anna Korzynska, Benoît Plancoulaine, Tomás Álvaro and Carlos López 92023) „Matrix Metalloproteinase-9 Expression Is Associated with the Absence of Response to Neoadjuvant Chemotherapy in Triple-Negative Breast Cancer Patients”, International Journal of Molecular Sciences 24, 11297. DOI: 10.3390/ijms241411297 [IF 5,6 ;140 pkt. MNiSW] Cooperation in consortium developing project BosomShield:
- Alessio Fiorin, Laia Adalid Llansa, Elena Goyda, Vincenzo Della Mea, Anna Korzynska, Shrief Abdelazeez, Ramon Bosch Príncep, Alba Fischer Carles, Noelia Gallardo Borràs, Marylène Lejeune, Daniel Mata Cano, Domenec Puig, Hatem A. Rashwan, Esther Sauras Colón, Mikel Relloso Ortiz de Uriarte, Laia Reverté Calvet, Carlos López Pablo (2024). Optimising Region of Interest Registration for Multiple-Tissue Whole Slide Images. In: Modat, M., Simpson, I., Špiclin, Ž., Bastiaansen, W., Hering, A., Mok, T.C.W. (eds) Biomedical Image Registration. WBIR 2024. Lecture Notes in Computer Science, vol 15249. Springer, Cham. DOI: 10.1007/978-3-031-73480-9_26
Słowa kluczowe:
analiza obrazów, segmentacja obrazów, obrazy mikroskopowe, rejestracja poklatkowa, analiza cyfrowych wielkoobszarowych obrazów, korekcja i standaryzacja zeskanowanych obrazów barwionych tkanek, patologia cyfrowa, wspomagana komputerowo morfometria ilościowa, badania dotyczące raka piersi, analiza obrazów cytologicznych, biologia ptaków, oologia
W Pracowni zrealizowano następujące projekty:
- “Zintegrowane podejście do diagnostyki i prognozowania nawrotu raka sutka w oparciu o biomarkery obrazu radiologicznego i patologicznego (tytuł oryginalny: A comprehensive CAD system based on radiologic- and pathologic-image biomarkers for diagnosis and prognosis of breast cancer relapse) , HORIZON-MSCA-2021-DN-01-01 MSCA Doctoral Network Project No. 10107322 akronim BosomShield; rozpoczęty w październiku 2022r
- “The segmentation method for cells segmentation in sequence of microscopic images” finansowany przez Narodowe Centrum Nauki (NCN), kierownik dr Anna Korzyńska, realizowany od 10.08.2008 do 09.06.2011;
- “Development of automatic quantitative methods for immunohistochemicaly stained thin tissue sections in investigation of immune response in breast cancer” finansowany przez Institute of Health Carlos III in Spain, kierownik dr Carlos Lopez z Molecular Biology and Research Section, Hospital Verge de la Cinta w Tortozie, realizowany od 1.01.2013 do 31.06.2016,
- “Automated analysis of tumor microenvironment in triple negative breast cancer without complete pathological response to neoadjuvant chemotherapy. Predictive factor of relapse” finansowany przez Institute of Health Carlos III in Spain, kierownik dr Merylene Lejeune z Molecular Biology and Research Section, Hospital Verge de la Cinta w Tortozie, realizowany od 1.01.2014 do 31.12.2016,
- „Web-based platform for the computer analysis of microscopic images to support the pathological diagnosis” finansowany przez Narodowe Centrum Badań i Rozwoju (NCBR), kierownik dr hab. Tomasz Markiewicz, z Politechniki Warszawskiej, realizowany od 27.09.2013 do 30.10.2016,
- „Narzędzie wspomagania histopatologa w analizie wirtualnych slajdów tkanek pacjentów z rakiem sutka barwionych immunohistochemicznie z użyciem DAB i Hematoksyliny” finansowany przez Narodowe Centrum Nauki (NCN), kierownik Łukasz Roszkowiak, realizowany od 2014 do 2019.
Rozprawy doktorskie:
- “Nowa metoda komputerowego wspomagania ilościowej oceny komórek w wielkoobszarowych obrazach preparatów tkankowych raka sutka barwionych immunohistochemicznie”, Łukasz Roszkowiak uzyskał stopień naukowy doktora nauk inżynieryjno-technicznych w 2023r.
W 2023 r. Łukasz Roszkowiak uzyskał stopień doktora nauk inżynieryjno-technicznych w dyscyplinie inżynieria biomedyczna, na podstawie przedstawionej rozprawy doktorskiej zatytułowanej „Nowa metoda wspomaganej komputerowo kwantyfikacji komórek w obrazach całych slajdów próbek tkanek raka piersi barwionych immunohistochemicznie”. Rozprawa ta koncentrowała się na metodach kwantyfikacji, segmentacji i klasyfikacji jąder komórkowych, obejmujących progowanie adaptacyjne, podział na klastry i przetwarzanie oparte na sztucznej inteligencji w celu zwiększenia dokładności i wydajności. Kluczowym osiągnięciem był program CHISEL, kompleksowy system zaprojektowany do precyzyjnej i powtarzalnej analizy komórek, usprawniający przepływy pracy w patologii cyfrowej. Poza CHISEL, badania dotyczyły metod interpolacji dla wirtualnych slajdów i strategii minimalizowania utraty obiektów, przyczyniając się do bardziej niezawodnych technik obrazowania diagnostycznego i biomedycznego. Promotorem w przewodzie doktorskim była dr hab. Anna Korzyńska, prof. IBIB PAN.
Wyposażenie:
W Pracowni dostępny jest mikroskop optyczny, pracujący w trybach jasnego pola lub fluorescencji. Posiada on możliwość cyfrowej rejestracji sekwencji z kontrolowanymi przez komputer przesłonami (dla UV i światła widzialnego) oraz stolikiem mikroskopu w osi Z. Wysokowydajna stacja obliczeniowa wyposażona w kartę graficzną NVIDIA RTX A5000, wysokiej klasy procesor Intel Pentium i 128 GB pamięci RAM, przeznaczona do wymagających zadań obliczeniowych i przetwarzania obrazu.